2023年国家级大学生创新训练计划项目结题:深度学习驱动的GH29酶氨基酸序列功能预测算法研究
发布时间:2024-11-25 阅读次数:
立项年份:2023年
项目成员信息: 指导教师信息:
邢柯-大二-计算机与信息技术学院 王睿--讲师-人工智能
薛美艳-大二-计算机与信息技术学院
王子洋-大二-计算机与信息技术学院
项目概况:
GH29岩藻糖苷酶,可以降解棕藻类植物(如海带、海藻等)的岩藻糖聚糖(Fucoidan)。在生物技术(食品工业、生物能源、环境净化)和药物开发(抗氧化,抗肿瘤,抗炎症)领域具有巨大的应用价值。然而在该酶所在家族3万多氨基酸序列中,已知其性质及功能的序列数量十分有限。
本项目与广州、英国等地的生物研究所开展合作,利用深度学习模型预测该家族内未知酶可能属于的类别及功能。
科研价值:
本项目研究的算法有助于生物界研究人员预测该家族内未知酶序列所属的类别,并推测出该酶所具有的性质以及功能,大大提高了预测效率,帮助GH29岩藻糖苷酶在生物技术和药物开发领域的快速应用。
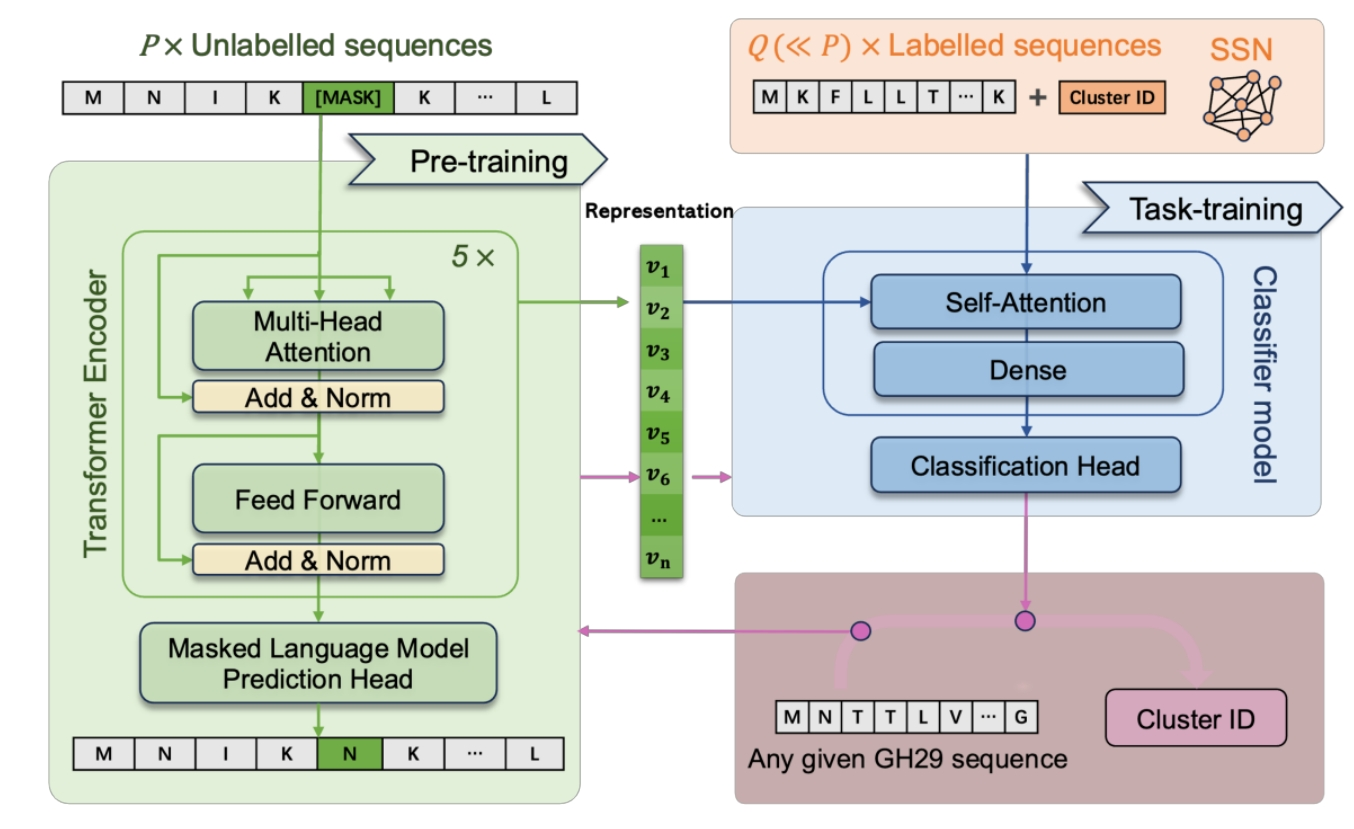
图 1 算法模型架构图
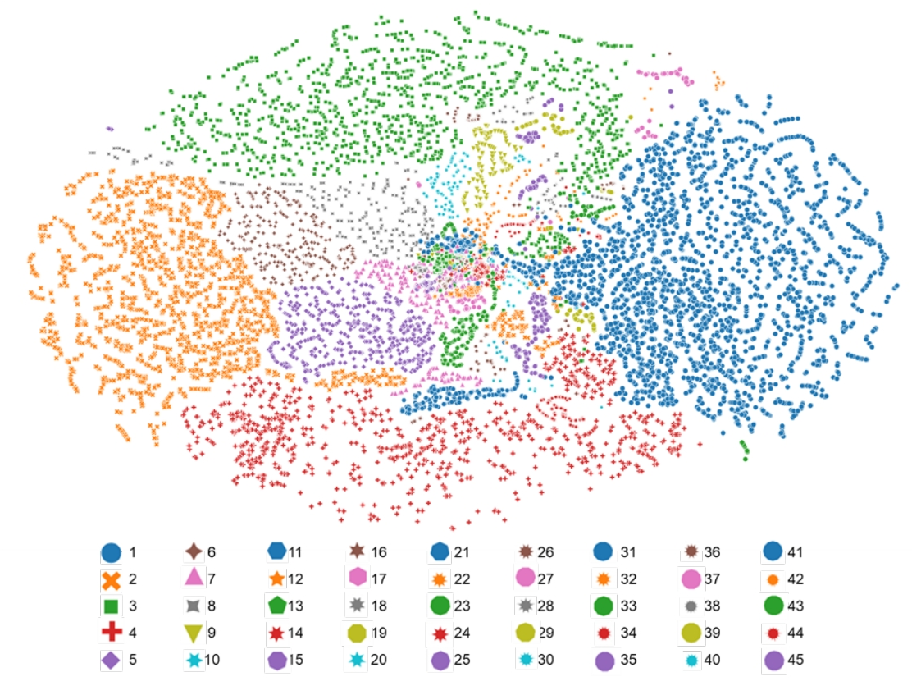
图 2 算法预测结果可视化图

图 3 模型对比图
项目创新点:
- 预训练+半监督学习,充分利用无标签数据
- 采用特征提取模型,泛化性强,并可对特征进一步开展研究
- 模型较小,节约算力
项目成果:
- 论文
合作撰写论文《Exploring the sequence-function space of microbial fucosidases》, 并投稿Communication Chemistry - Nature期刊。

图 4 论文原稿

图 5 审稿意见
图 6 审稿意见
- 专利
基于该算法申请专利,专利已提交国家专利局,项目负责人为第一发明人。

图 7 专利审查合格通知书
- 软件
基于研究的算法开发了供生物研究人员使用的交互友好的GH29家族蛋白质 序列功能预测软件。

图 8 软件演示图
- 软著
基于该软件撰写软著并已提交中国版权保护中心官网登记。
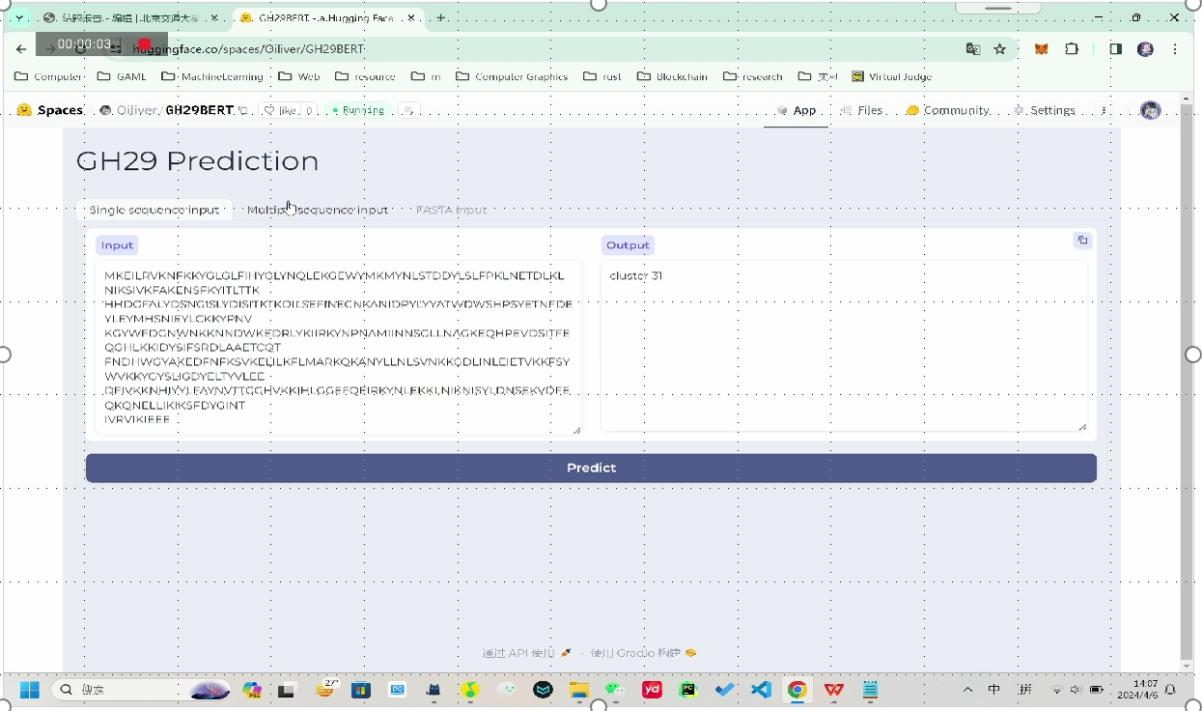
图 9 软件登记受理通知书


